Escolar Documentos
Profissional Documentos
Cultura Documentos
Metodos Autenticación Procariotas - Final - Rosa Aznar
Enviado por
julieth cTítulo original
Direitos autorais
Formatos disponíveis
Compartilhar este documento
Compartilhar ou incorporar documento
Você considera este documento útil?
Este conteúdo é inapropriado?
Denunciar este documentoDireitos autorais:
Formatos disponíveis
Metodos Autenticación Procariotas - Final - Rosa Aznar
Enviado por
julieth cDireitos autorais:
Formatos disponíveis
“Métodos de autenticación de microorganismos I.
Consideraciones generales y métodos más
utilizados en procariotas”
Rosa Aznar
Catedrática de Microbiología
Universitat de València
Directora de la CECT
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
Identificación / Autenticación: Autentificación
Cepa Cepa
desconocida conocida
Nuevo Cepa cedida Generación
Técnica elegida
Depósito por otra de nuevo lote
para identificar
Colección
Secuencias génicas, Sistemas Miniaturizados,
Control de Calidad
Sistemas Multiprueba, GC-FAME, MALDI-TOF, etc.
Técnica elegida
Autentificación
Identificación
para autentificar
Secuencias génicas, Sistemas Miniaturizados,
Sistemas Multiprueba, GC-FAME, MALDI-TOF, etc.
Datos
Datos
Comparación
con bases de
datos existentes
Comparación
Ne con bases de
a ga datos existentes
tiv tiv
osi a
P
Ne
va ga
siti tiv
Po a
Perfil no incluido
en la base de Posible nueva
Identificación especie
datos consultada
Autentificación Contaminación,
Necesidad de nuevas pruebas Autentificación deriva genética…
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
Procedimientos de control en procariotas
Viabilidad
Objetivos de cualquier
método de conservación Pureza microbiológica
Estabilidad de fenotipo y genotipo
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
¿Cuando se realiza el control?
Ø Cuando se recibe el material original
Pureza y viabilidad
Ø Después de la primera conservación (1er Lote)
Viabilidad, pureza y autenticidad (RNAr 16S siempre, otras)
Ø Después de cada nuevo lote generado
Viabilidad, pureza y autenticidad (FAME, RNAr 16S, depende
del grupo)
Además, con una periodicidad que depende del microorganismo,
realizamos controles de viabilidad post-almacenamiento
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
Procedimiento de control
Preparación y reposición de lotes
Comprobación de lote
Viales de trabajo
Cultivo activo en
condiciones óptimas de
crecimiento Suspensión celular con el
crioprotector adecuado
Lote homogéneo
Viales de reserva
Viales de reserva
2º almacén
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
Control de viabilidad
El control de viabilidad consiste en observar el
crecimiento de la cepa en su medio recomendado
• No utilizar nunca un medio selectivo/diferencial
• Las cepas liofilizadas/congeladas tienen una fase
lag mayor de lo normal. Prolongar el tiempo de
incubación (p.e. hasta 7 días para cepas que
crecen en 24 h)
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
Control de pureza
El control de pureza consiste en observar el aspecto y
morfología de las colonias en placa de medio sólido
• No utilizar nunca un medio
selectivo/diferencial
• Hacer la siembra por triple estría
• Hacer observaciones al microscopio
• Registrar la información morfológica
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
Control de autenticidad
Técnicas utilizadas en la CECT
Caracteres fenotípicos, sistemas miniaturizados
Análisis de la secuencia del gen de RNAr 16S
Análisis de la secuencia de otros genes “housekeeping”
Composición relativa de los ácidos grasos celulares (FAME)
Composición relativa de proteínas celulares (MALDI-TOF)
No se aplican todas las técnicas a todos los lotes
Se seleccionan según la especie / género / grupo microbiano al que
pertenecen (arqueas: secuencia rpoB; enterobacterias: FAMEs)
En los nuevos depósitos siempre incluimos la secuencia del RNAr 16S,
aunque apliquemos además otros métodos
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
Caracteres fenotípicos
Caracteres fenotípicos
Morfología (colonial y celular)
Test del KOH 3% à Gram positivo o Gram negativo
Citocromo oxidasa (reactivo N,n,n,n-tetrametil-p-fenilendiamina)
Catalasa (peróxido de hidrogeno al 30%)
Para confirmar pureza
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
Caracteres fenotípicos
VENTAJAS
Sistemas Miniaturizados • Menor espacio de almacenamiento
• Galerías API-Biomerieux • Caducidad más larga
• BBLCrystal • Estandarización
• Remel RapID • Facilidad de manejo
• Microgen • Resultados más rápidos
• Biolog
INCONVENIENTES
• etc.
• Limitado a patógenos,
fundamentalmente
•Base de datos limitada
• Estandarización (pH,
requerimientos iónicos, de factores
de crecimiento, etc.)
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
MALDI-TOF MS
Ø “Matrix Assisted Laser Desorption Ionization Time Of Flight Mass Spectrometry”
Ø Perfil de proteínas, mayoritariamente ribosomales (2-20 KDa), que se expresan
constitutivamente à técnica reproducible
Ø El perfil proteico no se ve afectado por las condiciones de cultivo o fase de
crecimiento en que se recoge la biomasa
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
MALDI-TOF MS
Perfil MALDI-TOF Lactobacillus casei CECT 475T
Espectro: 16/cepa Librería: normalización picos 16 espectros
Comparación de
BIOTYPER 1.1 librerías con base de
datos
Dendrograma
Identificación por valor numérico (log score)
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
MALDI-TOF MS
Autentificación en cepas de la CECT
Base de datos
MALDI-TOF MS
CECT
Ø Ventajas: Técnica reproducible y de fácil manejo
Ø Desventajas: Requiere de una base de datos previa
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
GC FAME
Ø “Fatty Acid Methyl Ester Gas Chromatography”
Ø Perfil de ácidos grasos característicos de especie bacteriana
Condiciones de cultivo pre-establecidas:
ü Medio de cultivo
ü Atmósfera
ü Temperatura
ü Tiempo de incubación
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
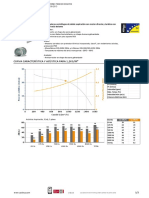
GC FAME
FID1 A, (E09B25.668\A0041041.D)
Volume: DATA File: E09B256.68A Samp Ctr: 4 ID Number: 1041
0.698
0.708
2.249
2.405
2.433
2.788
2.840
2.982
Type: QC Bottle: 3 Method: RTSBA6
Created: 11/25/2009 4:25:50 PM
2.207
2.775
Sample ID: CECT 115
2.055
25
3.045
1.332
RT Response Ar/Ht RFact ECL Peak Name Percent Comment1 Comment2
0.6980 630450 0.006 ---- 66.159 ---- < min rt
0.7077 1,19E+12 0.018 ---- 66.801 SOLVENT PEAK ---- < min rt Reference 20
12.123 4151 0.010 1.163 99.992 10:00 0.81 ECL deviates -0.001 0.003
Reference
13.317 21007 0.009 1.130 106.153 11:0 iso 3.97 ECL deviates -0.003 0.001
Reference
13.495 431 0.009 1.125 107.073 11:0 anteiso 0.08 ECL deviates 0.002 0.006
14.479 636 0.013 1.101 111.769 10:0 2OH 0.12 ECL deviates -0.001
15
1.671
15.122 1298 0.010 1.089 114.505 10:0 3OH 0.24 ECL deviates 0.003
16.004 8631 0.009 ---- 118.261 unknown 11.825 ---- ECL deviates 0.001
3.414
2.345
16.710 11326 0.009 1.059 121.099 11:0 iso 3OH 2.01 ECL deviates 0.002
1.600
17.763 821 0.018 ---- 125.005 unknown 12.502 ---- ECL deviates -0.001 Reference
18.097 3872 0.010 1.038 126.244 13:0 iso 0.67 ECL deviates 0.001 0.003
Reference 10
18.344 590 0.009 1.034 127.161 13:0 anteiso 0.10 ECL deviates 0.002 0.004
3.430
1.212
2.723
19.478 719 0.011 1.019 131.242 12:0 iso 3OH 0.12 ECL deviates 0.004
1.834 1.810
2.098
3.620
3.679
2.520
20.085 363 0.009 1.012 133.288 12:1 3OH 0.06 ECL deviates 0.004
2.278
3.480
1.634
1.512
3.076
20.548 22772 0.009 1.006 134.850 12:0 3OH 3.83 ECL deviates 0.002
3.103
4.242
Reference
2.190
1.948
1.350
1.697
1.448
1.966
2.152
1.776
2.008
2.315
3.018
2.365
20.976 2722 0.009 1.001 136.290 14:0 iso 0.46 ECL deviates 0.001 0.002 5
21.905 819 0.011 ---- 139.421 unknown 13.951 ---- ECL deviates -0.009 Reference -
22.071 23289 0.008 0.990 139.981 14:00 3.85 ECL deviates -0.002 0.001 0.5 1 1.5 2 2.5 3 3.5 4
22.493 27856 0.009 0.985 141.336 13:0 iso 3OH 4.59 ECL deviates 0.002
22.781 2312 0.011 0.983 142.257 13:0 2OH 0.38 ECL deviates 0.002
23.446 8867 0.009 0.976 144.388 15:1 iso F 1.45 ECL deviates -0.003 13:0 3OH/15:1
23.655 489 0.012 0.975 145.059 Sum In Feature 1 0.08 ECL deviates 0.003 iso H
Reference
24.048
24.334
25.199
217845
44783
2468
0.009
0.009
0.009
0.971
0.969
----
146.318
147.237
150.008
15:0 iso
15:0 anteiso
15:00
35.38
7.26
----
ECL deviates 0.000
ECL deviates -0.001
ECL deviates 0.001
0.001 -
Reference
0.001
Reference
MIDI Sherlock
27.230 3836 0.009 0.947 156.337 16:0 iso 0.61 ECL deviates 0.001 0.001
27.754 21281 0.008 0.943 157.970 16:1 w9c 3.36 ECL deviates -0.003 16:1 w7c/16:1
27.885 76204 0.009 0.943 158.378 Sum In Feature 3 12.01 ECL deviates -0.002 w6c
Reference
28.405
29.825
45746
30192
0.009
0.010
0.939
0.932
160.000
164.424
16:00
Sum In Feature 9
7.19
4.70
ECL deviates 0.000
ECL deviates -0.005
0.000
17:1 iso w9c Comparación
cromatogramas con
30.181 405 0.010 0.930 165.534 17:1 anteiso w9c 0.06 ECL deviates 0.001 Reference -
30.446 21044 0.009 0.928 166.359 17:0 iso 3.27 ECL deviates -0.001 0.001
Reference -
30.756 1381 0.010 0.927 167.325 17:0 anteiso 0.21 ECL deviates 0.000 0.001
31.025
34.144
1016
9707
0.010
0.009
0.926
0.914
168.165
177.940
17:1 w8c
18:1 w9c
0.16
1.48
ECL deviates 0.001
ECL deviates 0.000
base de datos
34.303 5014 0.010 0.914 178.439 Sum In Feature 8 0.77 ECL deviates -0.004 18:1 w7c -
Reference
34.799 1668 0.010 0.913 179.994 18:00 0.25 ECL deviates -0.001 0.001
Reference
36.789
42.419
3069
1055
0.011
0.014
0.909
----
186.394
204.810
19:0 iso 0.47
----
ECL deviates 0.001
> max rt
0.000
Matches:
ECL Deviation: 0.003 Reference ECL Shift: 0.002 Number Reference Peaks: 15
Library Sim Index Entry Name
Stenotrophomonas-maltophilia
Total Response: 623828 Total Named: 615892 RTSBA6 6.10 0.905 (Xanthomonas, Pseudomonas)
Percent Named: 98.73% Total Amount: 597913
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
GC FAME
Autentificación en cepas de la CECT
Ø Ventajas: Fácil manejo y bajo coste
económico
Ø Desventajas: Reproducibilidad
Base de datos dependiente de las condiciones de
GC FAME
cultivo empleadas y necesidad de una
CECT
base de datos previa
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
Secuenciación y análisis del gen RNAr 16S
Ø Gen universal
Ø Cobertura total en procariotas
Ø Resultados comparables interlaboratorio
Ø Técnica económica
Ø Sencilla (PCR – método Sanger)
Tamaño: 1522 bp à suficiente con 1000 bp en extremo 5’
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
Secuenciación y análisis del gen RNAr 16S
Bacterias 61.828
https://www.ezbiocloud.net
Arqueas 2.832
leBIBI QBPP
Herramientas públicas para el análisis
EzTaxon (http://eztaxon-e.ezbiocloud.net/)
BLAST (http://blast.ncbi.nlm.nih.gov/Blast.cgi)
RDP (http://rdp.cme.msu.edu/)
LeBibi (http://umr5558-bibiserv.univ-lyon1.fr/lebibi/lebibi.cgi)
SILVA (http://www.arb-silva.de/)
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
Secuenciación y análisis del gen RNAr 16S
Si > 98,7% pertenecen a la
misma especie
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
Secuenciación y análisis del gen RNAr 16S
u Secuencia parcial de otros genes: u Overall genome relatedness index (OGRI)
rpoB, rpoD, gyrB, recA, … ANI: Average Nucleotide Identity
dDDH: Digital DDH
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
20
Secuenciación y análisis de otros genes
Genes Housekeeping (genes estructurales codificantes de proteínas)
Ø Aplicación a grupos que no se resuelven con el RNAr 16S
Ø Transferencia Horizontal de Genes (THG)
Ø Base de datos incompleta
Ø Cepas de interés biotecnológico, clínico y fitosanitario
Ø Análisis con Blast (frente a base de datos GenBank/EMBL/DDBJ)
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
Gene Function Genus
atpD ATP synthase F1 Ensifer
dnaJ Chaperone with DnaK Neisseria, Ensifer, Thermus, Deinococcus
gap Glyceraldehydes-3-phosphate Ensifer
gapA Glyceraldehydes-3-phosphate Vibrio
groEL Post-translational modification, protein Streptococcus
turnover and chaperone genes
gyrB Gyrase B subunit Streptococcus, Vibrio, Bradyhizobium, Geobacter, Bradyrhizobium
luxABE Region of lux operon Vibrio, Photobacterium
pyrH Uridilate Kinase Vibrio
rctB Replication origin-binding protein Vibrio,
recA Recombinase A Vibrio, Ensifer, Bradyhizobium, Mycobacterium, Mycobacterium,
Geobacter, Bradyrhizobium
recN Recombination/repair protein Bordetella, Corynebacterium, Mycobacterium, Neisseria, Yersinia,
family Leuconostocaceae
rpoA RNA Pol alpha subunit Vibrio, Enterobacter, Lactobacillus
rpoB Transcription genes// RNA Pol Beta subunit Streptococcus, Vibrio, Bacillus, Legionella, Mycobacterium,
Pseudomonas, Staphylococcus, Bradyhizobium, Ensifer,
Geobacter, Halobacterium, Brucella
rpoD Factor sigma 70 RNA Pol Vibrio
sodA Inorganic ion transport and metabolism genes Streptococcus, Mycobacterium
toxR Transmembrane regulatory protein Vibrio
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
Consideraciones finales
ü Las colecciones microbianas albergan una enorme diversidad
à diferente estrategia a la hora de controlar la viabilidad,
pureza, autenticidad y estabilidad
ü No existen métodos universales (a veces ni dentro de la misma
especie) à con cada cepa hay que determinar las condiciones
más favorables
Bogotá 30/10/2018 Curso Internacional Colecciones de Microorganismos: aspectos técnicos y legales
Gracias por vuestra atención!!
24
Você também pode gostar
- U4 - Estimación Por Intervalos de Confianza y Tipos de MuestreoDocumento64 páginasU4 - Estimación Por Intervalos de Confianza y Tipos de MuestreoAlondraAinda não há avaliações
- Inspeccion Plan de EmergenciasDocumento4 páginasInspeccion Plan de EmergenciasJhonny PiconAinda não há avaliações
- ExposicionDocumento4 páginasExposicionjulieth cAinda não há avaliações
- Pr01-Plantilla Procedimiento Documentado HseqDocumento3 páginasPr01-Plantilla Procedimiento Documentado Hseqjulieth cAinda não há avaliações
- Extracción ADN linfocitosDocumento16 páginasExtracción ADN linfocitosjulieth cAinda não há avaliações
- MF AA4 Aplicacion y Diseno de Bases de Datos RelacionalDocumento18 páginasMF AA4 Aplicacion y Diseno de Bases de Datos RelacionalObed Marino Bonilla GomezAinda não há avaliações
- Formato Unico Licencia AmbientalDocumento1 páginaFormato Unico Licencia Ambientaljulieth cAinda não há avaliações
- Actividad de Apropiación Del ConocimientoDocumento2 páginasActividad de Apropiación Del Conocimientojulieth cAinda não há avaliações
- Norma BASCDocumento1 páginaNorma BASCjulieth cAinda não há avaliações
- Diagrama en BlancoDocumento1 páginaDiagrama en Blancojulieth cAinda não há avaliações
- Tabla de ContenidoDocumento4 páginasTabla de Contenidojulieth cAinda não há avaliações
- Actividad de Apropiación Del ConocimientoDocumento2 páginasActividad de Apropiación Del Conocimientojulieth cAinda não há avaliações
- Formato - Listado - Maestro - Control - Documentos-Hseq - EcovictalDocumento1 páginaFormato - Listado - Maestro - Control - Documentos-Hseq - Ecovictaljulieth cAinda não há avaliações
- Bol Insumos Nov 2015 PDFDocumento93 páginasBol Insumos Nov 2015 PDFEliecer CruzAinda não há avaliações
- Lab 4 AgricollaDocumento11 páginasLab 4 Agricollajulieth cAinda não há avaliações
- Análisis de productos químicos en una empresaDocumento13 páginasAnálisis de productos químicos en una empresaAlejandra Gómez Correa100% (4)
- Informe Abono OrganiDocumento16 páginasInforme Abono Organijulieth cAinda não há avaliações
- EXPLICACIONDocumento86 páginasEXPLICACIONjulieth cAinda não há avaliações
- Informe Bio Agricola Formulacion Inoculantes BiologicosDocumento8 páginasInforme Bio Agricola Formulacion Inoculantes Biologicosjulieth cAinda não há avaliações
- Plan HaccpDocumento2 páginasPlan Haccpjulieth cAinda não há avaliações
- MantequillaDocumento6 páginasMantequillajulieth cAinda não há avaliações
- Adulterntes de La LecheDocumento9 páginasAdulterntes de La Lechejulieth cAinda não há avaliações
- FORMATO INFORME VISITAS CoagronortesDocumento9 páginasFORMATO INFORME VISITAS Coagronortesjulieth cAinda não há avaliações
- Vac03210 PDFDocumento7 páginasVac03210 PDFjulieth cAinda não há avaliações
- PEDIOCInaDocumento3 páginasPEDIOCInajulieth cAinda não há avaliações
- AdulterantesDocumento5 páginasAdulterantesjulieth cAinda não há avaliações
- Diagnostico de Impactos Por Sector Industrial CementoDocumento8 páginasDiagnostico de Impactos Por Sector Industrial Cementojulieth cAinda não há avaliações
- FORMATO INFORME VISITAS CoagronortesDocumento9 páginasFORMATO INFORME VISITAS Coagronortesjulieth cAinda não há avaliações
- Químicos en Una EmpresaDocumento9 páginasQuímicos en Una Empresajulieth cAinda não há avaliações
- Vac03210 PDFDocumento7 páginasVac03210 PDFjulieth cAinda não há avaliações
- Metodos de Conservacion para Hongos PDFDocumento152 páginasMetodos de Conservacion para Hongos PDFSalvador Sandoval SosaAinda não há avaliações
- Antena Dipolo Doblada: Compensación de Impedancia y Mayor Banda PasanteDocumento14 páginasAntena Dipolo Doblada: Compensación de Impedancia y Mayor Banda PasanteedgarllanoAinda não há avaliações
- Semana 06 - Agregados para La Construccion 02Documento45 páginasSemana 06 - Agregados para La Construccion 02GROVER ESPINOZA MONARESAinda não há avaliações
- GARCÍA JURADO ARENAS - La Fonética Del Español (Pp. 11-17 y 117-123)Documento13 páginasGARCÍA JURADO ARENAS - La Fonética Del Español (Pp. 11-17 y 117-123)Luca TrifilettiAinda não há avaliações
- C3 - PER 2023 Monitoreo y Calidad de EnergiaDocumento26 páginasC3 - PER 2023 Monitoreo y Calidad de EnergiaBLIMAH PERU SACAinda não há avaliações
- Guia FarmacologiaDocumento21 páginasGuia FarmacologiaGabriela Ramos Noel0% (1)
- Capacitores Fijos y VariablesDocumento5 páginasCapacitores Fijos y VariablesAlberto Lencinas100% (2)
- Reconocimiento Geológico de Yura, Arequipa - Perú - Explorock - Blog de Las Geociencias y ExploraciónDocumento21 páginasReconocimiento Geológico de Yura, Arequipa - Perú - Explorock - Blog de Las Geociencias y ExploraciónBrayanChoquehuancaAinda não há avaliações
- Bugatti VeyronDocumento6 páginasBugatti Veyrontascoluminova0% (1)
- Memoria Descriptiva Relleno SanitarioDocumento3 páginasMemoria Descriptiva Relleno SanitarioLuis Alvaro Castillo VeloAinda não há avaliações
- 2 - Exposicion Gestion Del RiesgoDocumento35 páginas2 - Exposicion Gestion Del RiesgorlmcAinda não há avaliações
- CBD-1919-4M 1 5 150911081607Documento2 páginasCBD-1919-4M 1 5 150911081607Paco JonesAinda não há avaliações
- 1 (1) . - MICROBIOLOGIA UjapDocumento44 páginas1 (1) . - MICROBIOLOGIA Ujapmaria joseAinda não há avaliações
- Clase 4Documento25 páginasClase 4Victor TorresAinda não há avaliações
- Calefon Templatech 14 Litros1Documento6 páginasCalefon Templatech 14 Litros1luis gomez100% (1)
- Qué Son Las Ondas ElectromagnéticasDocumento7 páginasQué Son Las Ondas ElectromagnéticasJhon Fuentes GallegoAinda não há avaliações
- Semiotica 2Documento4 páginasSemiotica 2karenAinda não há avaliações
- DeberDocumento6 páginasDeberAnigaby MuñozAinda não há avaliações
- 1319-Texto Del Artículo-4979-1-10-20181108 PDFDocumento11 páginas1319-Texto Del Artículo-4979-1-10-20181108 PDFgonzaloagustin84Ainda não há avaliações
- Segundo Día Con Carlos Castaneda Y La TensegridadDocumento2 páginasSegundo Día Con Carlos Castaneda Y La TensegridadXavier SaAinda não há avaliações
- TCF - Ley de Caza (851-900)Documento101 páginasTCF - Ley de Caza (851-900)Madeline UlloaAinda não há avaliações
- Seminario TerapiaDocumento24 páginasSeminario TerapiaSamanta MartinezAinda não há avaliações
- Ostedyn para Bebés Mayores de 1 AñoDocumento2 páginasOstedyn para Bebés Mayores de 1 AñoGiulliana PaolaAinda não há avaliações
- Respeto A La Dignidad HumanaDocumento11 páginasRespeto A La Dignidad HumanaSámely Durán Antezana100% (1)
- CEBOLLA Elegir-EditarDocumento16 páginasCEBOLLA Elegir-EditarDaniela RamirezAinda não há avaliações
- Dificultad Respiratoria Aguda en El NiñoDocumento18 páginasDificultad Respiratoria Aguda en El NiñoMeliSsa DanielaAinda não há avaliações
- Ejer Cici OsDocumento9 páginasEjer Cici OsAndrea RamosAinda não há avaliações
- El Despliegue Del Jugar en La Práctica Psicomotriz para Libro Revista de Psm. Marina MarazziDocumento18 páginasEl Despliegue Del Jugar en La Práctica Psicomotriz para Libro Revista de Psm. Marina MarazziMaria Paula Chao AvilaAinda não há avaliações
- Informe 001 de La Planta AurelsaDocumento19 páginasInforme 001 de La Planta AurelsaMilagros Allcca NoaAinda não há avaliações
- Termoquímica: Estudio de la energía en reacciones químicasDocumento8 páginasTermoquímica: Estudio de la energía en reacciones químicastrim_84Ainda não há avaliações